因为是在conll03上做的NER任务,所以自然使用的是官方的评测脚本,那就是conlleval.perl。但是这个文件是用perl写成的,看起来很吃力,所以我就拿过来直接用,结果踩了不少坑。
首先需要配置perl环境,不过用conda或者pip可以直接下。
其次conlleval.perl接受的输入是这个样子的:
El 0 0
consejero 0 0
de 0 B-MISC
Economía B-MISC I-MISC
Industria I-MISC I-MISC
Comercio I-MISC I-MISC
Manuel B-PER B-PER
Amigo I-PER I-PER注意上面使用的是BIO标注法,而不是BIOES标注法。如果你模型的输出是BIOES标注的,需要把E(end)转化为I,S(single)转化为B。
最坑的一点,是需要把所有的O标注都转化为0,然后才能写到文件里。
按照上面的要求写好文件之后,在你的python脚本里调用如下命令即可。
os.system("perl {} < {} > {}".format(FLAGS.perl_path, FLAGS.predict_path, FLAGS.metric_path))出来的结果应该是类似于这样的:
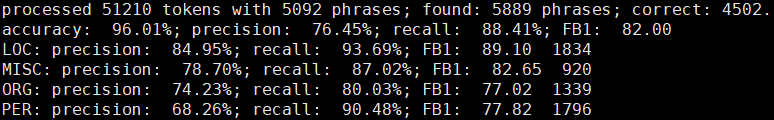
如果出来的格式不太一样,那就是你写到文件里的标签还是不符合要求了。